
図1.福井大学総合実験研究支援センターのバイオ実験機器部門では、新たに先端研究支援3分野を1)プロテオーム研究分野、2)トランスクリプトーム研究分野、3)分子細胞生物学研究分野に決め、重点的な実験機器整備及び技術開発を目指している。プロテオーム研究は最終表現形の多様性を解明する学問であるが、今後ゲノミクス研究と双璧をなす分野に成長する可能性がある。このスライドはマウスの3種の臓器における発現蛋白の網羅的解析手段としての2D-DIGE法の結果であり、各臓器で共通の発現を示す蛋白(オレンジ)と臓器特異的発現をする蛋白(赤又は緑)は色素の違いで明瞭である。
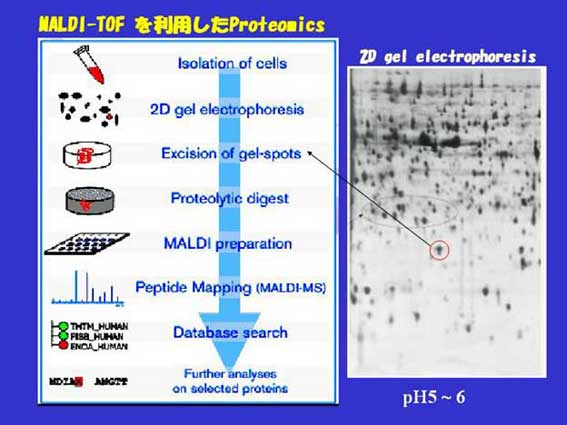
図2.組織特異的発現を示す蛋白や、薬剤、温度、紫外線、ストレス、ホルモン、成長増殖因子、サイトカインなどの刺激に応答する蛋白発現の同定がプロテオーム研究の中心的課題である。丸で囲まれた蛋白スポットが如何なる蛋白であるかを明らかにする方法が示されている。消化された蛋白からのペプチドは固有の質量の一次関数である。これを高性能MALDI-TOF MSによって計測し、データベースで検索すると、既知の蛋白の一次関数との相同性から同定できる。
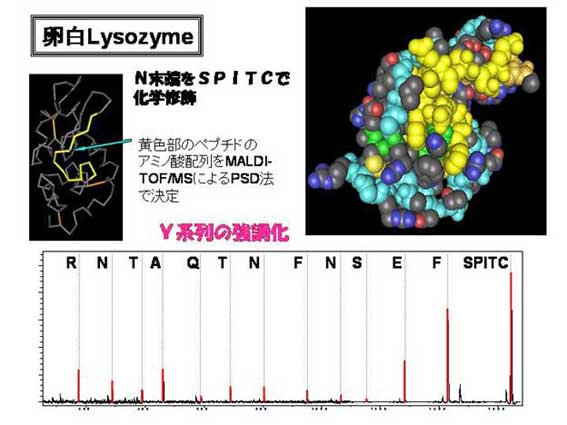
図3.しかし、その検索の確率は30~40%に留まっている。それは、一次関数が遺伝子の配列から導き出されたものであるからである。生体の蛋白は様々な修飾を受けて質量数が遺伝子から予測されたものと違うことがその原因である。そのため、ある蛋白をトリプシンなどの消化酵素で分解して得たペプチドのアミノ酸配列を部分的に決定することでその問題を解消できる可能性がある。そのためにMALDI-TOF MSによるPSD法が利用できる。このスライドでは、PSDによる配列決定を高能率で行うためのSPITC処理後の配列決定法を示している。
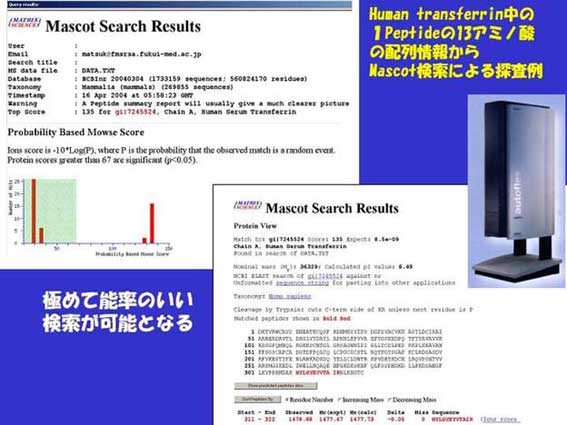
図4.ヒト血清内鉄輸送蛋白のトランストランスフェリンの一つのアミノ酸配列を決めたものを検索QueryとしてMASCOT検索したもので、chain Ahuman serum transferrinが高い確率で合致したことが分かる。しかもたった12アミノ酸の配列データのみでそれが実現できたことを示している。我々は、検索効率を著しく向上させることを実証したものと考えてる。このように、発現差を示す未知の蛋白を知り、それがどのような蛋白であるかを効率よく突き止めるための技術基盤を提供できる準備がほぼ完了し、利用者に恩恵を与えるものと期待している。

